Description
工作流程发布,不足交流探讨及改进
工作流程发布,不足交流探讨及改进
#柱状图
#=========================================================================
# 加载包
#=========================================================================
library(ggplot2)
library(dplyr)
library(reshape2)
#=========================================================================
# 1.library(ggplot2)
library(dplyr)
library(reshape2)
# ===================== 数据 =====================
eggnog <- data.frame(
Category = c("A","B","C","D","E","F","G","H","I","J","K","L","M","N","O","P","Q","R","S","T","U","V","W","Y","Z"),
disease = c(1331.92,583.42,59792.40,12647.23,72533.57,17147.12,
58640.01,31475.03,36986.05,37400.36,58142.47,67299.68,
55828.29,9119.68,32528.88,45813.37,34376.89,0,
146233.98,50492.20,17621.21,17423.12,279.45,28.24,766.37),
healthy = c(1979.61,1166.96,61561.81,11042.在操作时发现,由于个人习惯喜欢在tmux中操作,所以有时候停止进行,但是会产生临时文件
临时文件不可以直接rm删除
首先,查看文件的进程
lsof .nfs000000003074ec5a0f349c35全基因组选择的交叉验证,BWGS包会直接提供一个预测结果(rrBLUP包也会提供),可以用来绘制相关性散点图来直观显示模型的预测性能
做GWAS表型很多,不可能一个一个作图,所以对表型数据进行批量分析,利用AI写了一个R代码
用的表型数据形式如下:
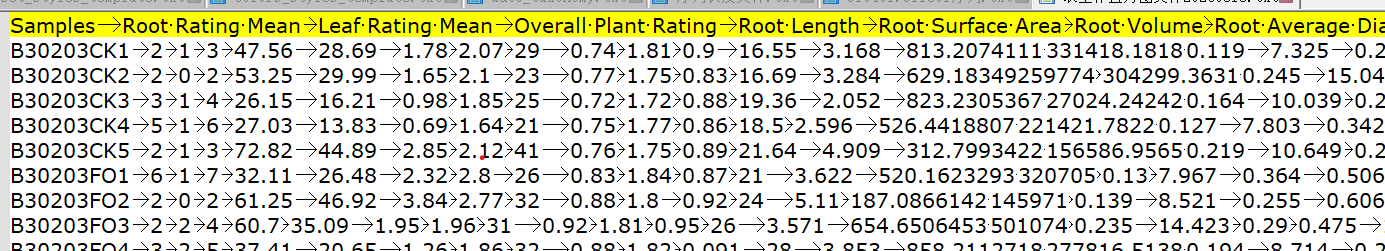
第一列为样本为,之后每一列是一个表型,中间用制表符分隔开。
一、直方图分析
群体间遗传分化指数(FST ):是种群分化和遗传距离的一种衡量方法,分化指数越大,差异越大。FST 居于0~1之间,越接近1表示两个群体之间分化程度越大,受选择程度越高,反之亦然。
FST = (HT-HS)/ HT
HS : 亚群体中的平均杂合度
HT : 复合群体中的平均杂合度
FST 值的取值范围是[0,1],最大值为1表明两个群体完全分化,最小值为0表明群体间无分化。
在实际的研究中FST 值为 0-0.05 时说明群体间遗传分化很小,可以不做考虑;
为0.05-0.15时,表明群体间存在中等程度的遗传分化;
为0.15-0.25时群体间存在较大的遗传分化;
为0.25以上的时候群体间就存在很大的遗传分化了。